Hipótesis del mecanismo de Replicación Experimento de Hersey y Chase.
-
Upload
lucia-montes-luna -
Category
Documents
-
view
286 -
download
0
Transcript of Hipótesis del mecanismo de Replicación Experimento de Hersey y Chase.


Hipótesis del mecanismo de Replicación

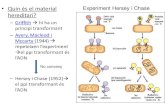
Experimento de Hersey y Chase

DNA marcado con 15N y 14N separado por un gradiente de densidad
DNA marcado con 15N y 14N separado por un gradiente de densidad
(a)(a)
(b)(b)

Experimento de Hersey y Chase II

Topoisomerasas tipo I y II

Desenrollamiento de la cadena mediante topoisomerasas

Tipos de DNA topoisomerasas
Type Substrate Examples
Type IA Single-stranded DNA Escherichia coli topoisomerases I and III; yeast and human topoisomerase III; archaeal reverse gyrase
Type IB Single-stranded DNA Eukaryotic topoisomerase IType II Double-stranded DNA E. coli topoisomerases II (DNA gyrase) and IV;
eukaryotic topoisomerases II and IV

Actividad de topoisomerasas
• Las DNA topoisomerasas no desenrollan la doble hélice.
• Lo que hacen es resolver el problema topológico contratacando el sobre-enrollamiento que de otra manera tendría la molécula por la progresión de la horquilla de replicación.
• El resultado es que la hélice puede ser “unzipped” poniendo las dos hebras aparte sin que la molécula tenga que rotar.

Modelos de replicación en DNA circular

El proceso de la replicación
• Iniciación. Involucra el reconocimiento de la posición en dónde empieza la replicación de una molécula de DNA.
• Elongación. Eventos de la horquilla de replicación en dónde es sintetizada una hebra complementaria.
• Terminación. Poco entendia

Iniciación
• No es un proceso al azar.• Empieza en una secuencia conocida como origen
de replicación• Generalmente se inician dos horquillas de
replicación de cada origen (bidireccional).• Un genoma circular bacteriano presenta un solo
origen de replicación.• En eucariontes hay multiples orígenes para cada
cromosoma. (levadura ~300).

Replicación bidireccional

Replicación de un cromosoma circular tomando la forma de Replicación de un cromosoma circular tomando la forma de
(a)(a) (b)(b)

Inicio de la replicación en E. coli
• El origen de replicación de E.coli se conoce como oriC.
• Presenta 245 pb de DNA.
• Contiene dos motivos cortos repetidos, uno de nueve nucleótidos (nonámero), cinco copias y otro de 13 nucleótidos (tridecámero) 3 copias.




• La proteína DnaA se une a las regiones ricas en AT
• DnaA debe estar acoplada a ATP.
• 30 moléculas de DnaA se unen a oriC
• La unión ocurre cuando el DNA esta superenrollado negativamente, situación normal en E. coli.

• El resultado de la unión de DnaA a la doble hélice que esta se funde.
• El mecanismo exacto no se conoce pero parece ser el estrés de torción inducido por DnaA.
• La fusión de la hélice es promovida por HU, la proteína más abundante que ayuda a empacar al DNA de E. coli.

• Después de la fusión son reclutadas las proteínas DnaBC, formando el complejo pre-priming.
• DnaC tiene un papel transitorio y puede ser que ayude a DnaB a unirse.
• DnaB es una helicasa, que puede romper pares de bases.
• Incrementa la región de hebra sencilla en el origen.

Orígenes de replicación el levadura
• Se les llama ARSs (autonomously replicating sequences)
• 200 pb• Presenta regiones discretas o subdominios• ORS (secuencia de reconocimiento del origen), 40
pb que es reconocida por un grupo de 6 proteínas, el ORC (complejo de reconocimiento del origen).
• No es precisamente un complejo de iniciación pues sigue unido después de iniciada la replicación.

Estructura del origen de replicación de levadura

Origen de replicación en eucariontes superiores
• No se ha podido encontrar secuencias ni homólogas ni análogas a orígenes de replicación en eucariontes superiores.
• Podría ser que la replicación se iniciara en estructuras proteínicas que tienen posiciones específicas en el núcleo.

• Se describió por Aladjem et al., (1998) una región de 8 kb que conservó su potencialidad de iniciar la replicación a alta frecuencia al clonarla en genoma de chimpancés.
• Proteínas con secuencias homólogas a ARSs se han encontrado también.

Elongación o alargamiento
• Dificultades– Las dos hebras tienen que ser copiadas al
mismo tiempo y la polimerasa solo copia de 5’--> 3’
– La hebra retardada debe copiarse de manera discontinua produciendo fragmentos cortos.
– La DNA polimerasa necesita cebadores que proporcionen extremos 3’

DNA pol en eucariontes y procariontes
• Sintetizan polinucleótidos en sentido 5’-->3’
• Requiere de un cebador o primer
• Tienen actividad de exonucleasa 3’-->5’ (no todas)

Sintesis de DNA dependiente de un molde

DNA polymerases involved in replication of bacterial and eukaryotic genomes
Exonuclease activities Enzyme Subunits 3’-->5’ 5’-->3’ FunctionBacterial DNA polymerase
DNA polymerase I 1 Yes Yes DNA repair, replicationDNA polymerase III At least 10 Yes No Main replicating enzyme
Eukaryotic DNA polymerases
DNA polymerase 4 No No Priming during replicationDNA polymerase 2 Yes No Mitochondrial DNA replicationDNA polymerase 2 or 3 Yes No Main replicative enzymeDNA polymerase At least 1 Yes No Required for detection of DNA damage during genome
replicationDNA polymerase 1 or 2? ? ? Required for attachment of cohesin proteins which hold
sister chromatids together until the anaphase stage of nuclear division
Bacteria and eukaryotes possess other DNA polymerases involved primarily in repair of damaged DNA. These enzymes
include DNA polymerases II, IV and V of Escherichia coli and the eukaryotic DNA polymerases , ζ, η , and ι. Repair processes are described in Section 14.2.

Gen estructural*Gen estructural*
SubunidadesSubunidades
MMrr
Exonucleasa 3'-->5' Exonucleasa 3'-->5' (corrección de errores)(corrección de errores)
Exonucleasa 5'-->3'Exonucleasa 5'-->3'
Velocidad de polimerización Velocidad de polimerización (nucleótidos/s)(nucleótidos/s)
Procesividad (nucleótidos Procesividad (nucleótidos añadidos antes de disociarseañadidos antes de disociarse
DNA polimerasasDNA polimerasas
II
polpol A A
11
103,000103,000
Si Si aaaaa
SiSi
16-20 16-20 aaa
3-2003-200
IIII
pol pol BB
≥ ≥ 44
88,00088,000
Sí Sí aaaaa
NoNo
~7 ~7 a
≥≥10,00010,000
IIIIII
pol pol CC
≥ ≥ 1010
~900,000~900,000
SíSíaa aaaaa
NoNo
250-250-10001000aaa
≥≥500,000500,000
Comparación de las DNA pol de E. coli
Comparación de las DNA pol de E. coli

25,000
10,000 130,000
α (polC) - Sínt esis de DNAε (dnaQ) - Correcci ón 3 '➝5'θ - ensamblaje?
εθ
αα εθ
τ τ
εθ
αα εθ
τ τ
δ δ
γ γ
εθ
αα εθ
τ τ
δ δ
γ γβ β β β
Centro catalítico Masa = 165,000
Pol III* Masa = 470,000
Masa = 750,000
Masa = 900,000
Pol III'
Holoenzima
Consiste de 2 centros + 2τ (dnaX)τ provoca la dimerización
Incrementa laprocesividad
Sintesis de DNA
Consiste de Pol II*+ complejo γδ
El complejo γδ se une al molde
Consiste de Pol III'+ la subunidad β (dnaN)
Sintetiza las hebraslider y rezagada
Aislamiento de diferentes formas de actividad Pol III

Estructura de subunidad tau

DNA pol de eucariontes
• Son al menos 9 polimerasas• Se nombran con letras griegas (igual que las
subunidades de la pol III).• La replicasa es la • Trabaja en conjunto con el antígeno nuclear
de proliferación (PCNA)• PCNA equivale a la subunidad de la DNA
pol de E. coli.

Síntesis discontinua del DNA

Cebando la síntesis del DNA

Helicasa

Estructura de la helicasa

SSB

Cebando y sintetizando
la hebra rezagada

Síntesis en paralelo de
la hebra líder y
rezagada

Unión de los fragmentos de Okazaki

Endonucleasa FEN1

Dos modelos de acompletar la replicación resagada


Topología de la terminación en cromosomas circulares.

Secuencias de termino en e coli

Coesinas

Problema del primer cebador

Extensión del cromosoma por la terlomerasa

Terminación de la expresnión

Células senesentes

Sequences of telomere repeats and telomerase RNAs in various organisms
Species Telomere repeat sequence Telomerase RNA template sequence
Human 5’-TTAGGG-3’ 5’-CUAACCCUAAC-3’Oxytricha 5’-TTTTGGGG-3’ 5’-CAAAACCCCAAAACC-3’Tetrahymena 5’-TTGGGG-3’ 5’-CAACCCCAA-3’
Oxytricha and Tetrahymena are protozoans which are particularly useful for telomere studies because at certain developmental stages their chromosomes break into small fragments, all of which have telomeres: they therefore have many telomeres per cell (Greider, 1996).

Fases del ciclo celular

Cdc6 p

Ciclinas mitóticas